https://www.163.com/dy/article/G8OKP6M50532ROLT.html
#基因_信号通路
https://www.genecards.org/
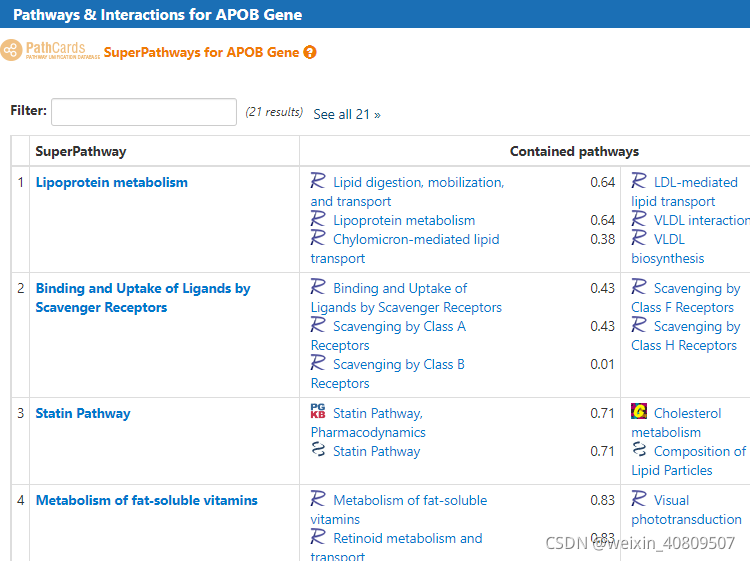
#由目标通路中查找通路中的基因?
https://pathcards.genecards.org/
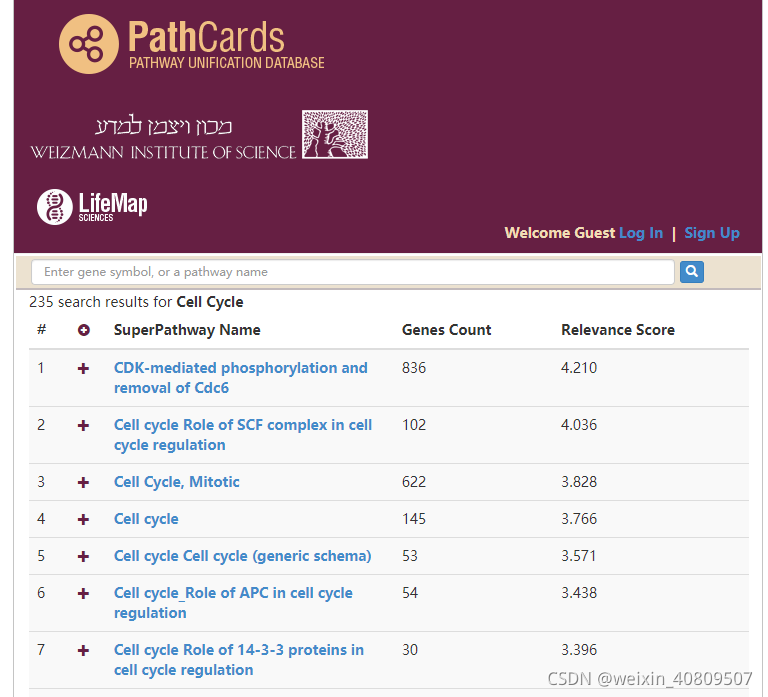
#蛋白相互作用分析
- 蛋白相互所有分析(PPI)
- STRING的使用以及网络分析
#共表达分析
- GEO中查看是否有相关基因敲除或者过表达的表达数据
- 如果是肿瘤研究的话,那直接就使用TCGA的数据就可以来进行研究。https://www.cbioportal.org/




















 506
506











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








