绘制tRNAscan-SE生成的二级结构
tRNAscan-SE是常用的tRNA预测软件,它生成的结果中以.ss结尾的文件保存着tRNA的二级结构,如何将它画出来呢?
这里我们可以修改.ss文件的内容,并分割成单条序列,然后借用ViennaRNA软件画图。步骤如下:
1 修改文件并分割:
原始.ss文件中是这样的内容:
HG.trna1 (36861-36932) Length: 72 bp
Type: Val Anticodon: GAC at 33-35 (36893-36895) Score: 58.9
* | * | * | * | * | * | * |
Seq: AGGGATATAACTCAGCGGTAGAGTGTCACCTTGACGTGGTGGAAGtCATCAGTTCGAGCCTGATTATCCCTA
Str: >>>>>>>..>>>>.......<<<<.>>>>>.......<<<<<.....>>>>>.......<<<<<<<<<<<<.
HG.trna2 (72828-72901) Length: 74 bp
Type: Asp Anticodon: GTC at 35-37 (72862-72864) Score: 65.8
* | * | * | * | * | * | * |
Seq: GGGATTGTAGTTCAATCGGTcAGAGCACCGCCCTGTCAAGGCGGAAGcTGCGGGTTCGAGCCCCGTCAGTCCCG
Str: >>>>>>>..>>>>.........<<<<.>>>>>.......<<<<<.....>>>>>.......<<<<<<<<<<<<.
.trna3 (73586-73672) Length: 87 bp
Type: Ser Anticodon: GGA at 35-37 (73620-73622) Score: 73.6
* | * | * | * | * | * | * | * | *
Seq: GGAGAGATGGCCGAGTGGTtcAAGGCGTAGCATTGGAACTGCTATGTAGGCTTTTGTTTACCGAGGGTTCGAATCCCTCTCTTTCCG
Str: >>>>>>>..>>>...........<<<.>>>>>.......<<<<<.>>>>>>....<<<<<<.>>>>>.......<<<<<<<<<<<<.
所有的tRNA二级结构都在一个文件中,我们需要把内容改成如下形式:
>HG.-trnL-211411-211491
GCCTTGGTGGTGAAATGGTAGACACGCGAGACTCAAAATCTCGTGCTAAAGAGCGTGGAGGTTCGAGTCCTCTTCAAGGCA
(((((((..(((..........))).(((((.......))))).(((....)))..(((((.......)))))))))))).
>HG.-trnD-72828-72901
GGGATTGTAGTTCAATCGGTCAGAGCACCGCCCTGTCAAGGCGGAAGCTGCGGGTTCGAGCCCCGTCAGTCCCG
(((((((..((((.........)))).(((((.......))))).....(((((.......)))))))))))).
>HG.-trnP-451564-451638
CGAGGTGTAGCGCAGTCTGGTCAGCGCATCTGTTTTGGGTACAGAGGGCCATAGGTTCGAATCCTGTCACCTTGA
(((((((..((((..........)))).(((((.......))))).....(((((.......)))))))))))).
这里注意需要把每条序列单独放到一个文件中(.flod),有多少条序列就要生成多少个文件。
2 使用RNAplot画图
RNAplot -o svg < file.flod
到这里会生成svg格式的图片:
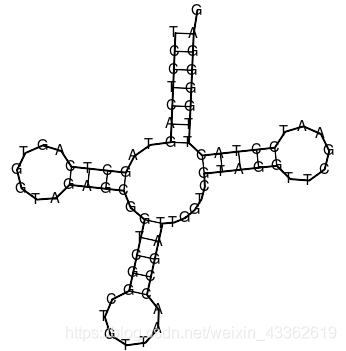
以上两步已经整合到perl脚本,可以到群文件获取(QQ群:636121790),命令如下:
perl get_rnaflod_from_trnascan_ss.pl -i sample.ss
生成后的svg格式图片可以参考之前的文章内容进行修改:Perl : 线粒体tRNA二级结构的美化(mitos2)
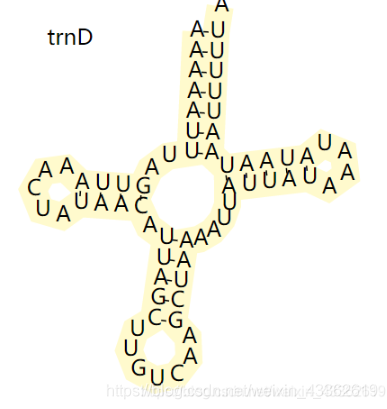
有问题的小伙伴可加群咨询~
























 5370
5370

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








