1 运行bwa将read比对到参考基因组
# 创建一个名为bwa_test的目录,如果该目录不存在的话
mkdir ~/bwa_test -p
# 进入bwa_test目录
cd ~/bwa_test/
# 下载参考基因组文件(注释掉的部分表示该行代码被注释掉,不会执行)
#wget ftp://ftp.ncbi.nlm.nih.gov/genomes/all/GCA/000/012/525/GCA_000012525.1_ASM1252v1/GCA_000012525.1_ASM1252v1_genomic.fna.gz
# 解压缩下载的基因组文件(注释掉的部分表示该行代码被注释掉,不会执行)
#gunzip GCA_000012525.1_ASM1252v1_genomic.fna.gz
# 从指定路径复制基因组文件到当前目录
cp /disk1/shares/Seqs/GCA_000012525.1_ASM1252v1_genomic.fna .
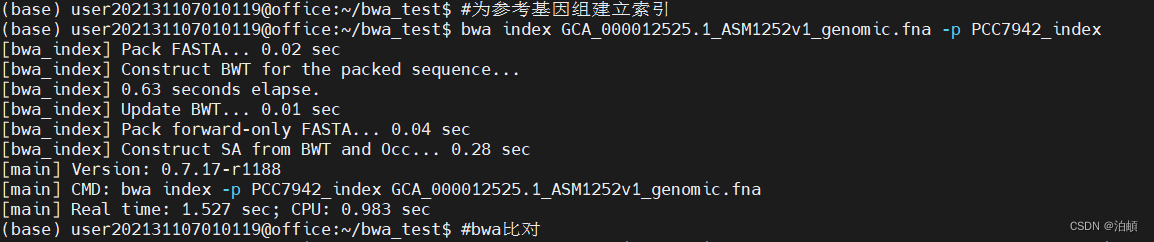
# 为参考基因组建立BWA索引
bwa index GCA_000012525.1_ASM1252v1_genomic.fna -p PCC7942_index
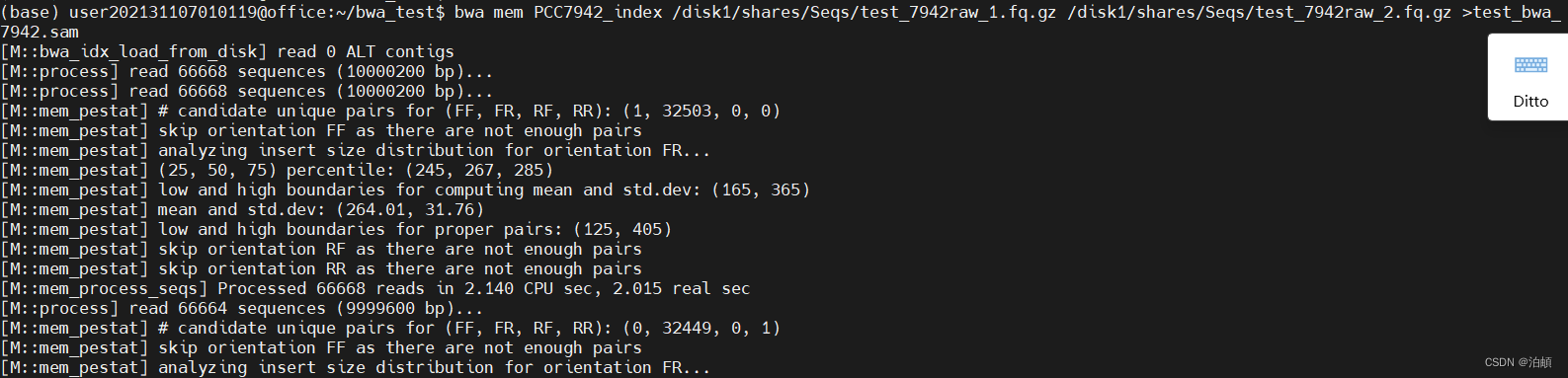
# 使用BWA进行比对,将比对结果保存为SAM文件
bwa mem PCC7942_index /disk1/shares/Seqs/test_7942raw_1.fq.gz /disk1/shares/Seqs/test_7942raw_2.fq.gz >test_bwa_7942.sam
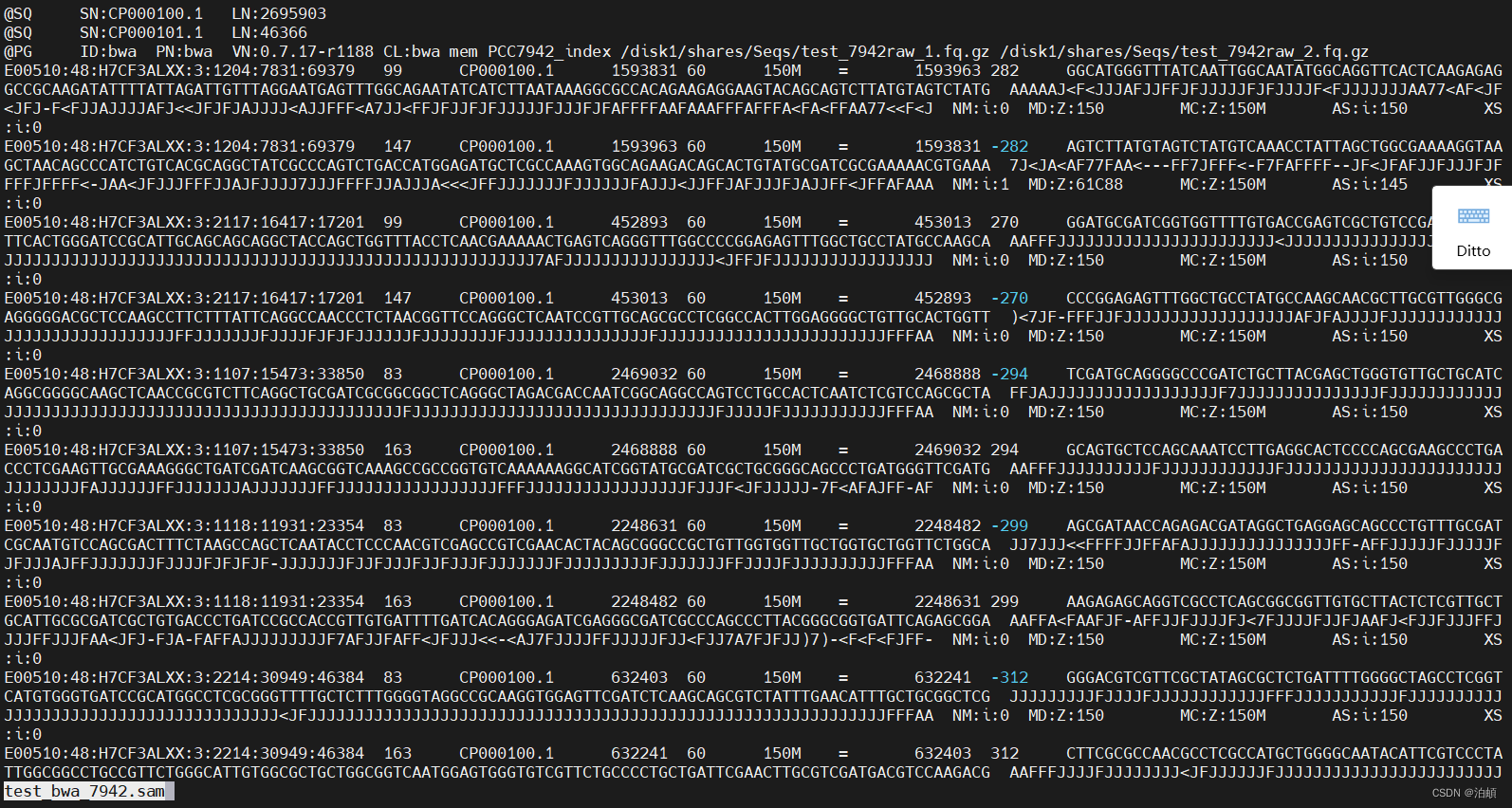
# 查看生成的SAM文件的内容,可以逐页浏览
less test_bwa_7942.sam
2 运行Bowtie2将read比对到参考基因组 安装运行
# 创建一个名为bowtie2_test的目录,如果该目录不存在的话
mkdir bowtie2_test
# 进入bowtie2_test目录
cd bowtie2_test/
# 从指定路径复制参考基因组文件到当前目录
cp /disk1/shares/Seqs/GCA_000012525.1_ASM1252v1_genomic.fna ./
# 列出当前目录下的文件,以确认文件是否成功复制
ll
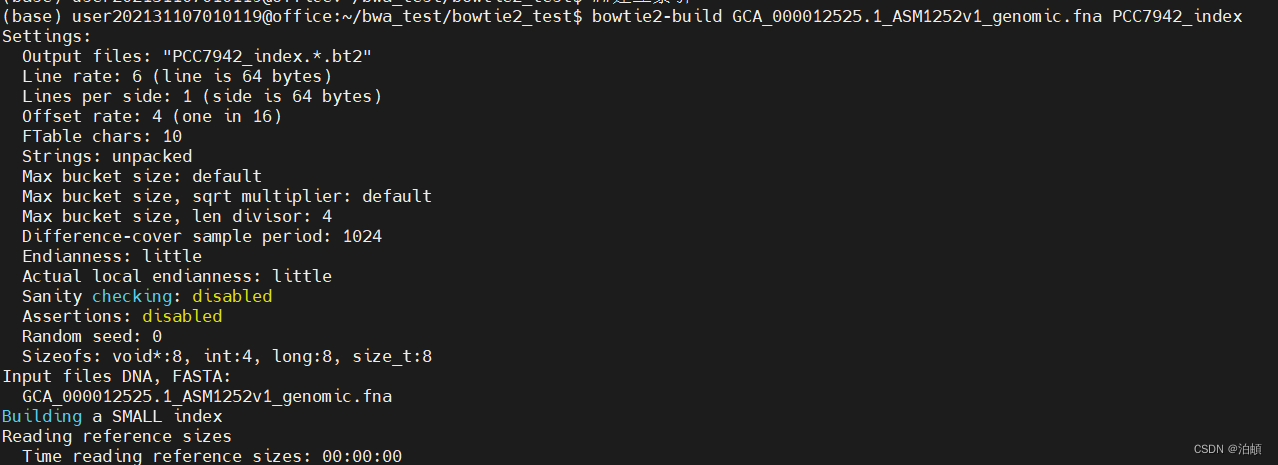
# 为参考基因组建立Bowtie2索引
bowtie2-build GCA_000012525.1_ASM1252v1_genomic.fna PCC7942_index
# 再次列出当前目录下的文件,以确认索引是否成功建立
ll
# 使用Bowtie2进行比对,将比对结果保存为SAM文件
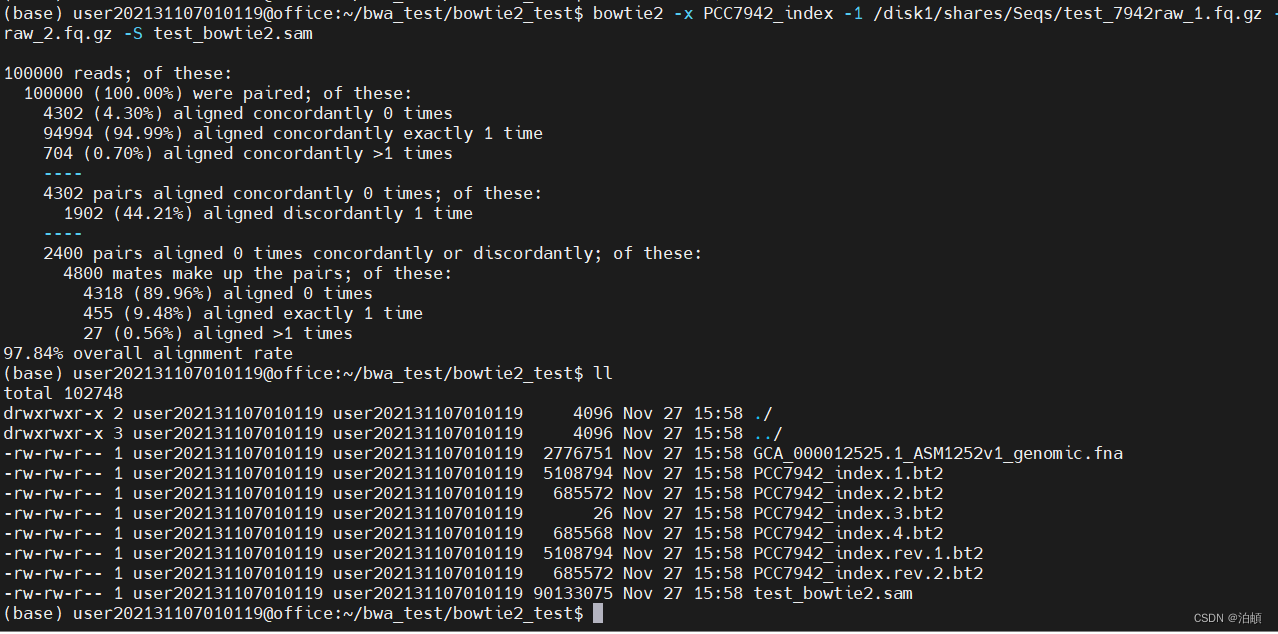
bowtie2 -x PCC7942_index -1 /disk1/shares/Seqs/test_7942raw_1.fq.gz -2 /disk1/shares/Seqs/test_7942raw_2.fq.gz -S test_bowtie2.sam
# 再次列出当前目录下的文件,以确认SAM文件是否成功生成
ll
3 比较bwa和bowtie2运行速度
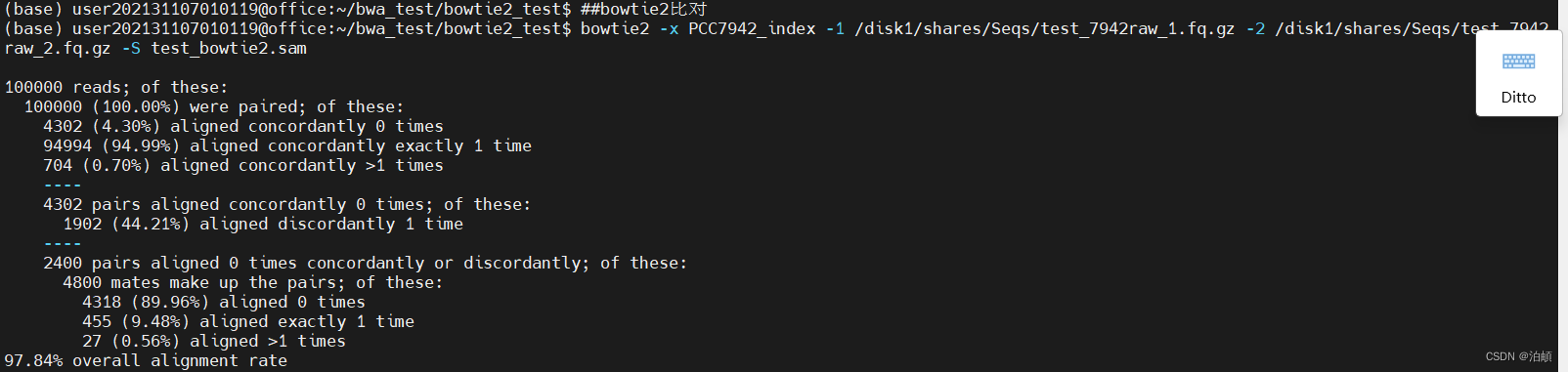
time bowtie2 -x PCC7942_index -1 /disk1/shares/Seqs/test_7942raw_1.fq.gz -2 /disk1/shares/Seqs/test_7942raw_2.fq.gz -S test_bowtie2.sam
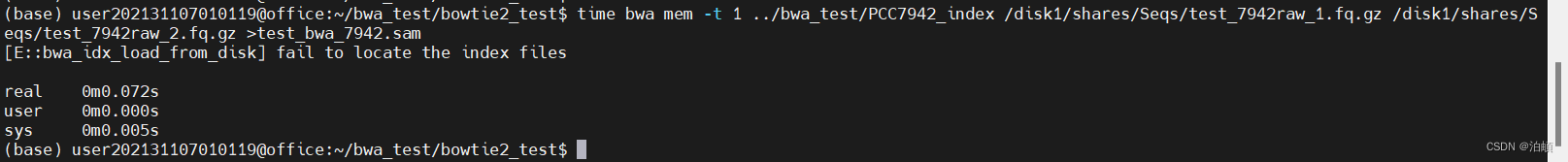
time bwa mem -t 1 ../bwa_test/PCC7942_index /disk1/shares/Seqs/test_7942raw_1.fq.gz /disk1/shares/Seqs/test_7942raw_2.fq.gz >test_bwa_7942.sam
- BWA
- Bowtie2






















 5511
5511











 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








