背景介绍
CNV检测已成为全基因组分析的常规内容,并显著提升了阳性诊断率。然而,由于实验室水平和所使用软件的差异,目前仍难以全面、准确地覆盖CNV的检测与细节分析。尤其在数据分析环节,目前尚无开源软件能够在性能优越的同时,全面解决这一问题。以流行的CNVnator为例,这是一款基于Read Depth(RD)原理的拷贝数变异检测软件,主要用于全基因组数据分析。CNVnator不仅能在人群中进行拷贝数变异检测和基因分型,还能根据需求鉴定一些非典型CNV。
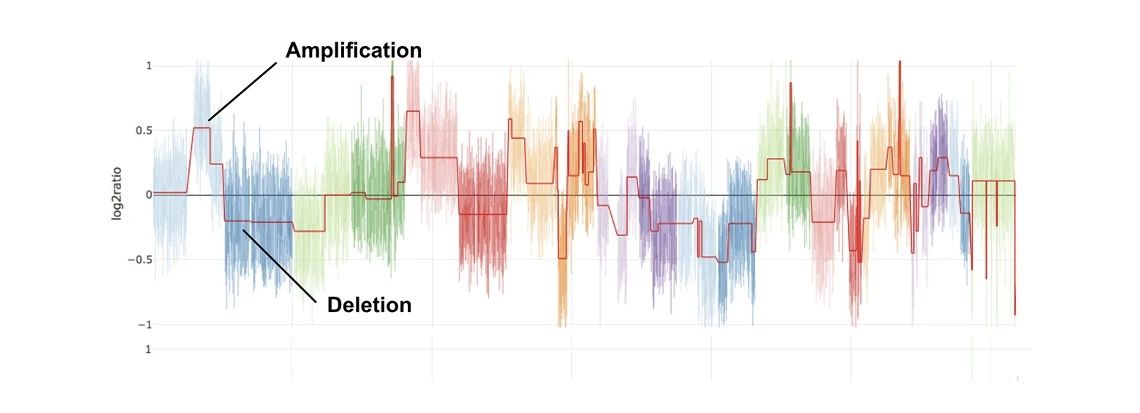
总体而言,CNVnator具备较高的灵敏度、较低的错误发现率、并且其断点检测分辨率较高。然而,作为一款经典软件,CNVnator在应对现今多平台测序数据和新一代参考基因组等最新数据类型时,已表现出一定的局限性。
1.适用场景
CNVscope是Sentieon推出的一款基于机器学习的全基因组CNV分析检测模块。该模块主要用于检测大于5kb的拷贝数增加或缺失,方法是通过分析reads的深度信息,并结合断点检测等其他特征进行拷贝数判断。
2.环境必备
- 软件授权:License须开通CNV模块权限
- 软件下载:https://insvast-download.oss-cn-shanghai.aliyuncs.com/Sentieon/release/sentieon-genomics-202308.03.tar.gz
- 模型下载:https://insvast-download.oss-cn-shanghai.aliyuncs.com/Sentieon/release/ml_model/SentieonIlluminaWGS2.2.bundle
3.分析流程
运行两个独立的命令来进行 CNV 检测和应用机器学习模型。输入的BAM文件应该来自已经完成比对和去重复的流程。
sentieon driver -t NUMBER_THREADS -r REFERENCE -i DEDUPED_BAM \
--algo CNVscope --model SentieonIlluminaWGS2.2.bundle/cnv.model TMP_VARIANT_VCFsentieon driver -t NUMBER_THREADS -r REFERENCE --algo CNVModelApply \
--model SentieonIlluminaWGS2.2.bundle/cnv.model -v TMP_VARIANT_VCF VARIANT_VCF注意:使用同一个模型进行CNVscope和CNVModelApply操作很重要,如果使用不同的模型,CNVModelApply计算会报错。
4.参数说明
以下是输入参数说明:
- NUMBER_THREADS:计算中将使用的计算机线程数。我们建议该数量不要超过您系统中可用的计算核心数。
- REFERENCE:参考FASTA文件的位置。您应确保该参考与映射阶段使用的参考相同。
- DEDUPED_BAM:输入BAM文件的位置。
- TMP_VARIANT_VCF:CNVscope变异调用输出的位置和文件名。这是一个临时文件。
- VARIANT_VCF:变异调用输出的位置和文件名。将创建一个相应的索引文件。该工具将使用.gz扩展名输出压缩文件。
5.结果说明
最终输出的VCF文件使用CN注释来表示CNVscope机器学习模型调用的每个区域的拷贝数状态。CNVscope调用的可能拷贝数状态从0到4,其中CN=4表示拷贝数状态等于或大于4。
附录:研发细节
在CNVscope的开发过程中,建立新一代的CNV真集用于训练和测试是最为关键的一步。目前常用的CNV真值集主要来自GIAB的HG002项目和千人基因组计划。然而,由于这些真值集依赖于早期的短读长技术,特别是在低复杂度区域的准确性存在一定问题。
随着测序技术的进步,尤其是长读长测序的发展,使得染色体级别的全基因组组装成为可能。例如,HG002 T2T(端到端)联盟最近宣布完成了HG002所有46条染色体的完整组装,使得样本的结构变异(SV)表征更加准确。同样,Human Pangenome Reference Consortium(人类泛基因组参考联盟)也发布了多个高质量的组装结果,为业内研究者开发最新的分析工具提供了基础。
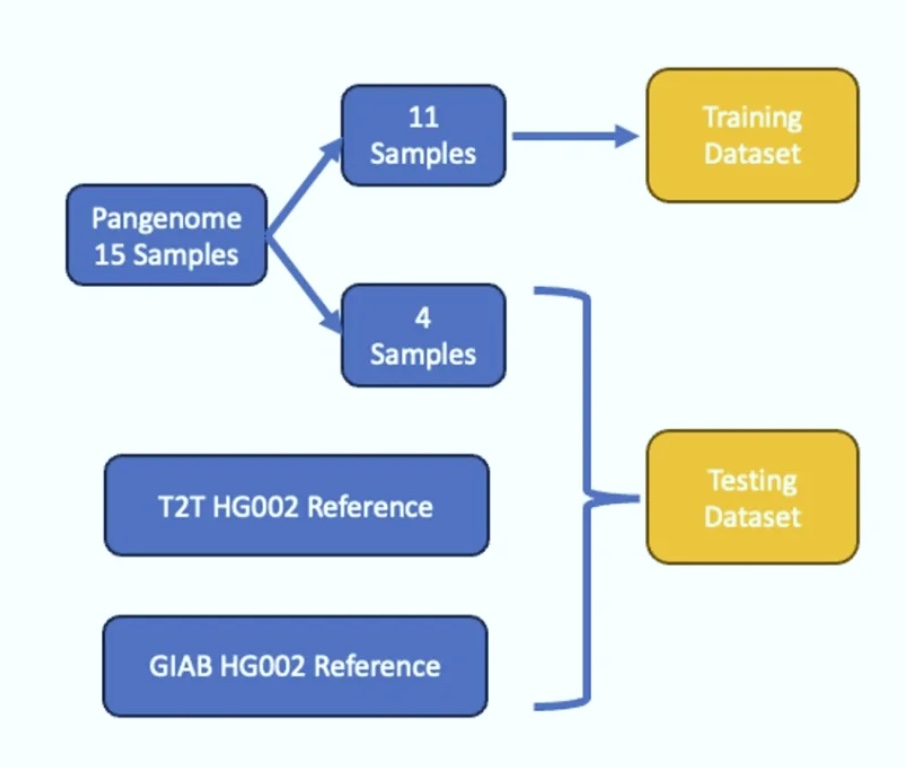
Sentieon团队在此次开发中,主要采用了最新的HG002 T2T真集以及泛基因组项目中的15个样本。这些真集利用了第三代测序数据,大大提升了结构变异检测的准确性。我们从这些真集中提取了超过5kb的DUP(重复)和DEL(缺失)变异,作为CNVscope开发的真集数据。其中,11个图形基因组样本作为训练集,其余4个样本和T2T数据作为测试集。所有数据均来自约30x深度的全基因组测序。
为展示准确度,我们将CNVscope与先前提到的CNVnator (v0.4.1) 和Illumina开发的DRAGEN CNV (v4.2) 在不同数据集上进行了逐一对比。
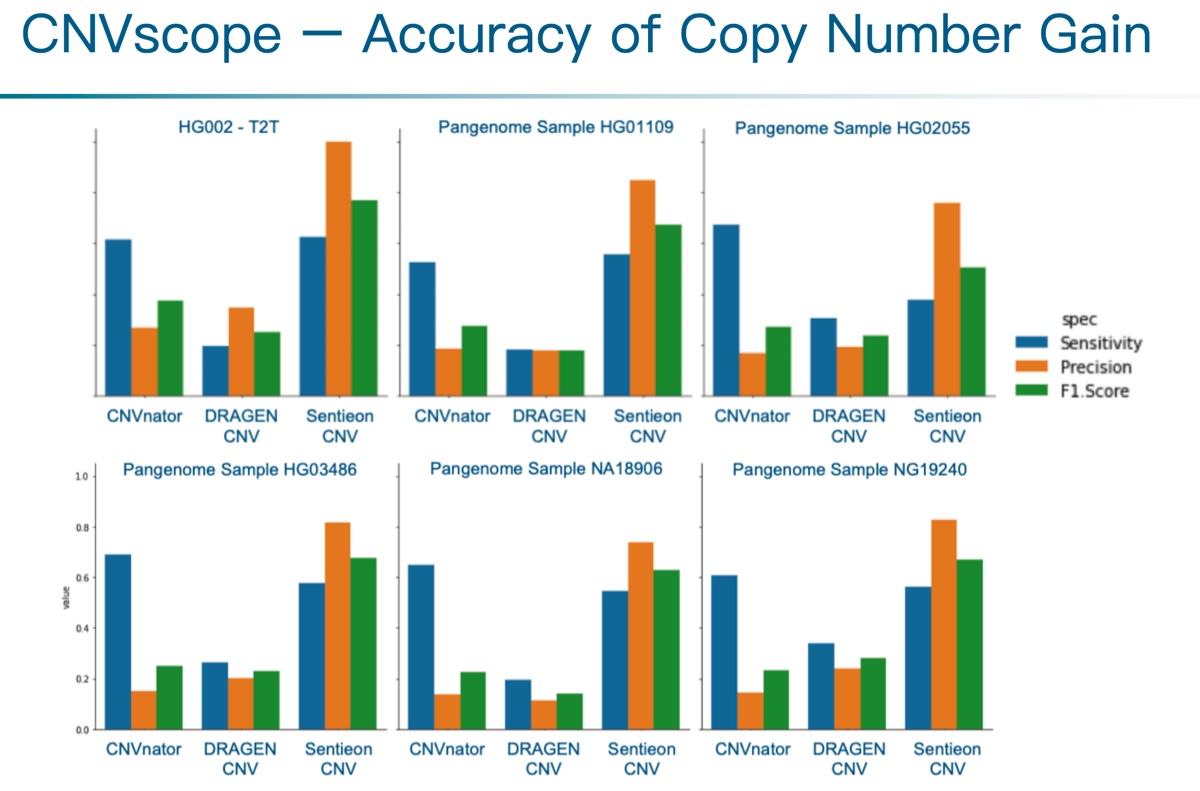
图1 拷贝数重复事件
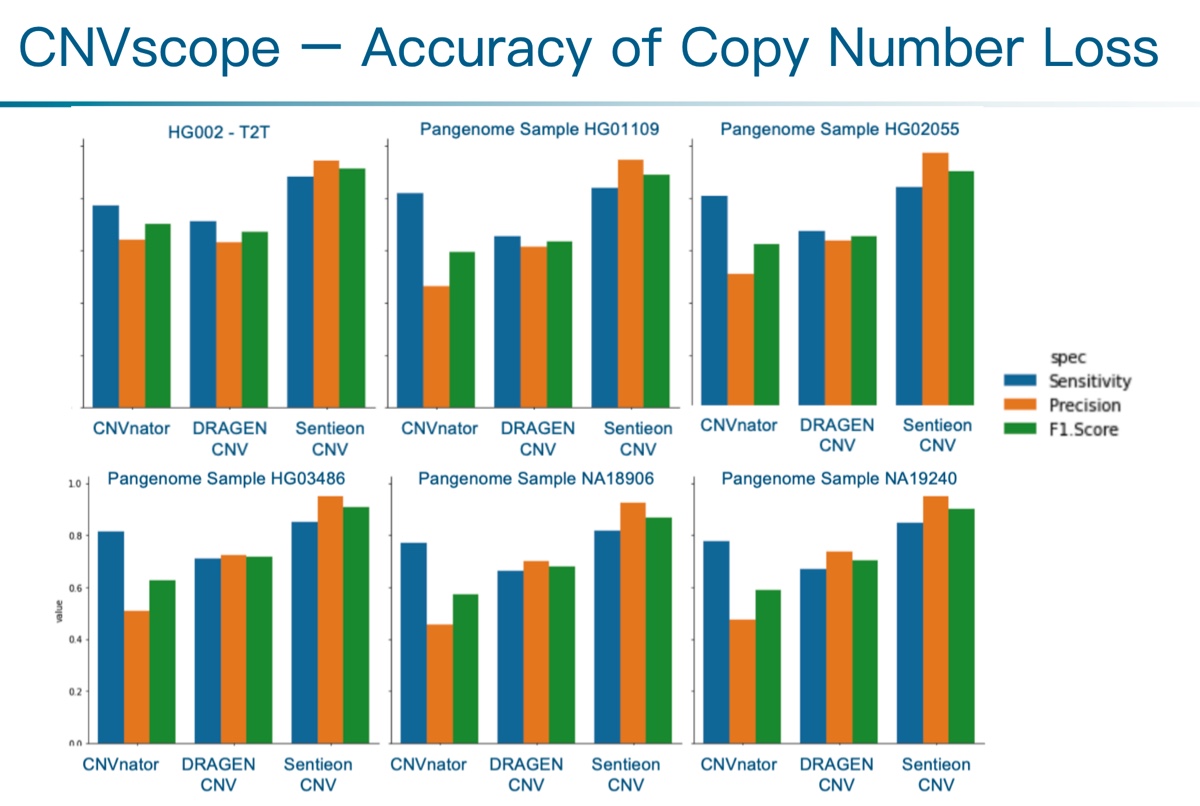
图2 拷贝数缺失事件
从结果来看,Sentieon CNVscope 在WGS中的表现相较于现有的CNV工具,展现出极高的准确性(F1值)。目前,CNVscope正处于持续迭代阶段,当前主要聚焦于检测大于5kb的胚系WGS事件,而小于5kb的复制和缺失则由DNAscope的结构变异检测模块处理。
未来,CNVscope还将推出适用于外显子组测序(WES)数据和体细胞CNV的分析流程。
























 2139
2139

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








