IGV变异可视化设置要点
IGV基因组浏览器(interactive genome visualization)是目前最常用的基因组学可视化工具,本文简单介绍一下NGS生信进行SNV、INDEL变异可视化的常用设置和基础操作。
变异可视化
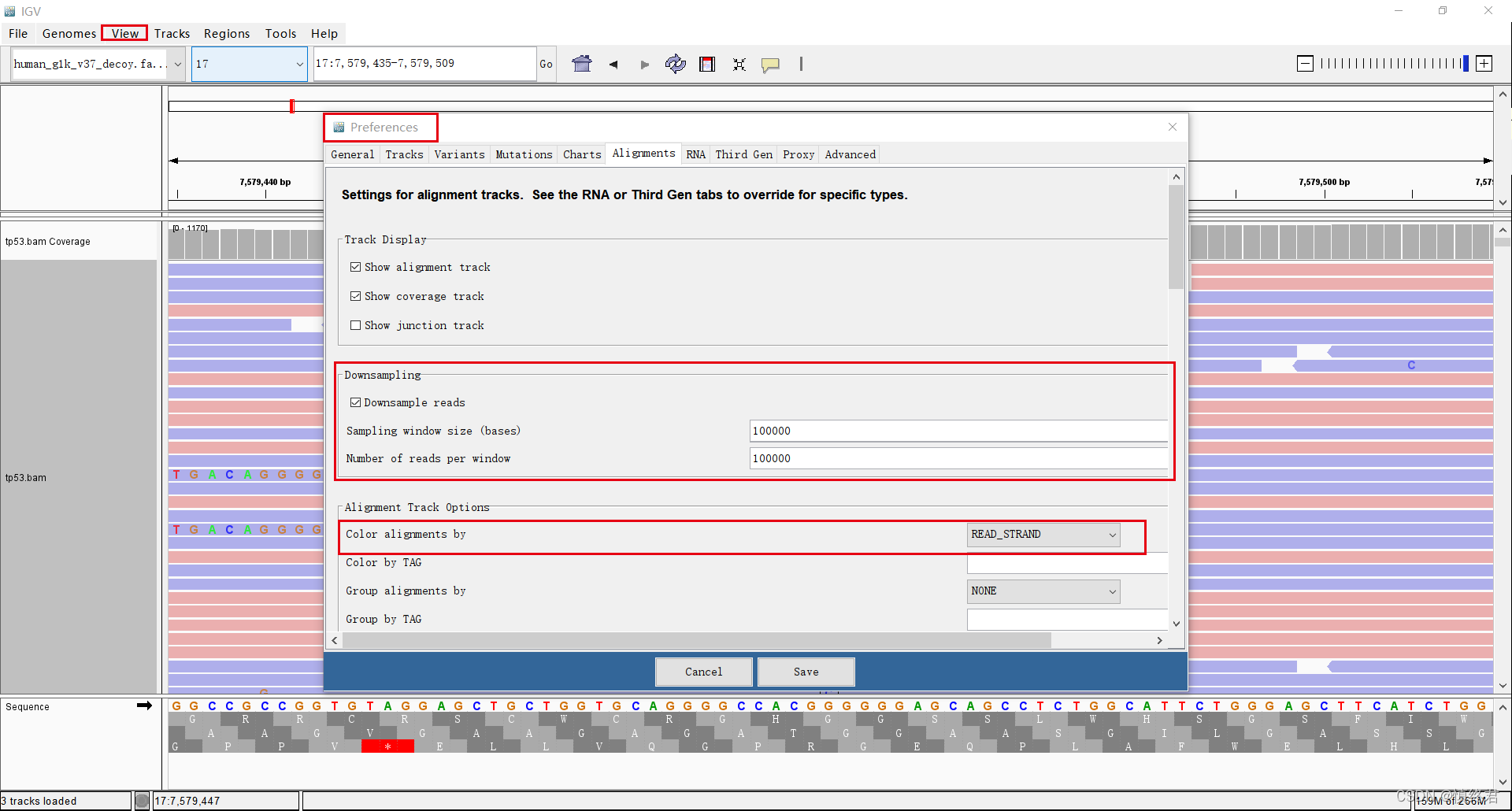
- 点击菜单栏View-Preferences-Alignments,在Downsampling栏目,取消Downsample reads,或者下面两个文本框填入想要的reads数。
解释:Downsampling降采样,在高深度测序区域只显示部分reads,对于低频突变特别不友好,我甚至见过一个10几条reads支持的低频变异连一条支持reads都不显示的情况。如果需要查看高深度测序区域变异情况最好取消降采样。
- Alignment Track Options栏目,Color alignments by选择“READ_STRAND”,这样不同链的reads会用红蓝双色分别显示,有助于可视化变异的链偏好性
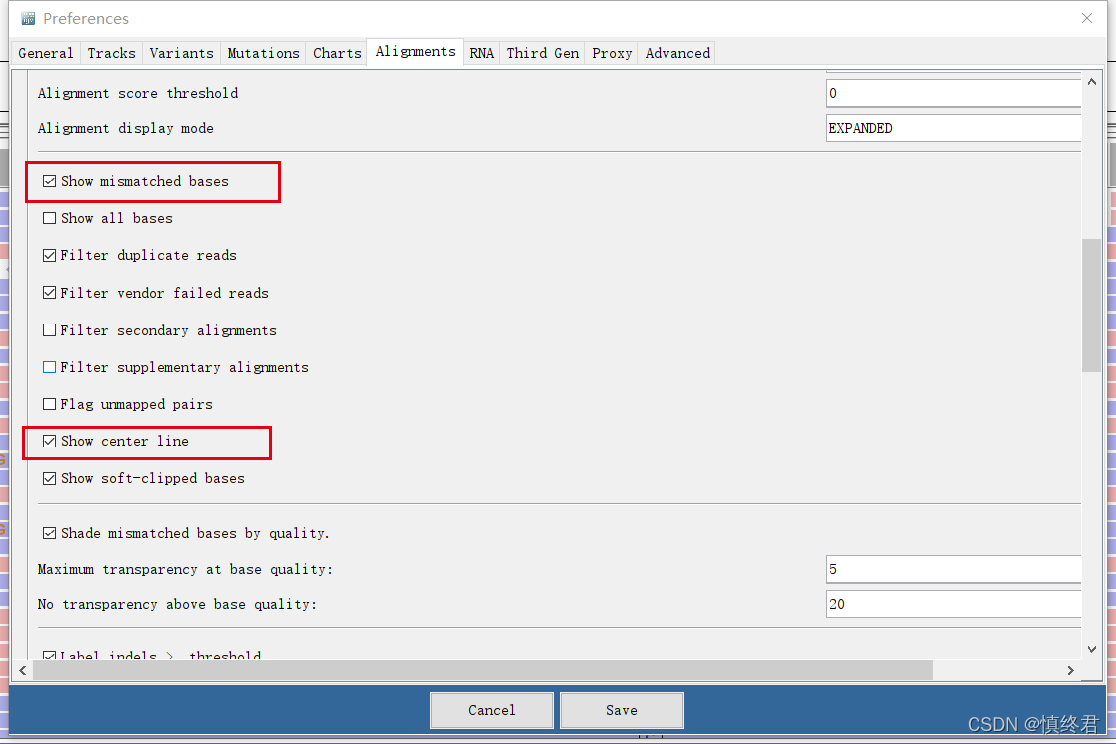
- Show mismatched bases,显示不匹配的碱基,变异可视化的基础,必选
- Show center line,显示中心线,有助于定位到当前展示的变异,必选
基本操作
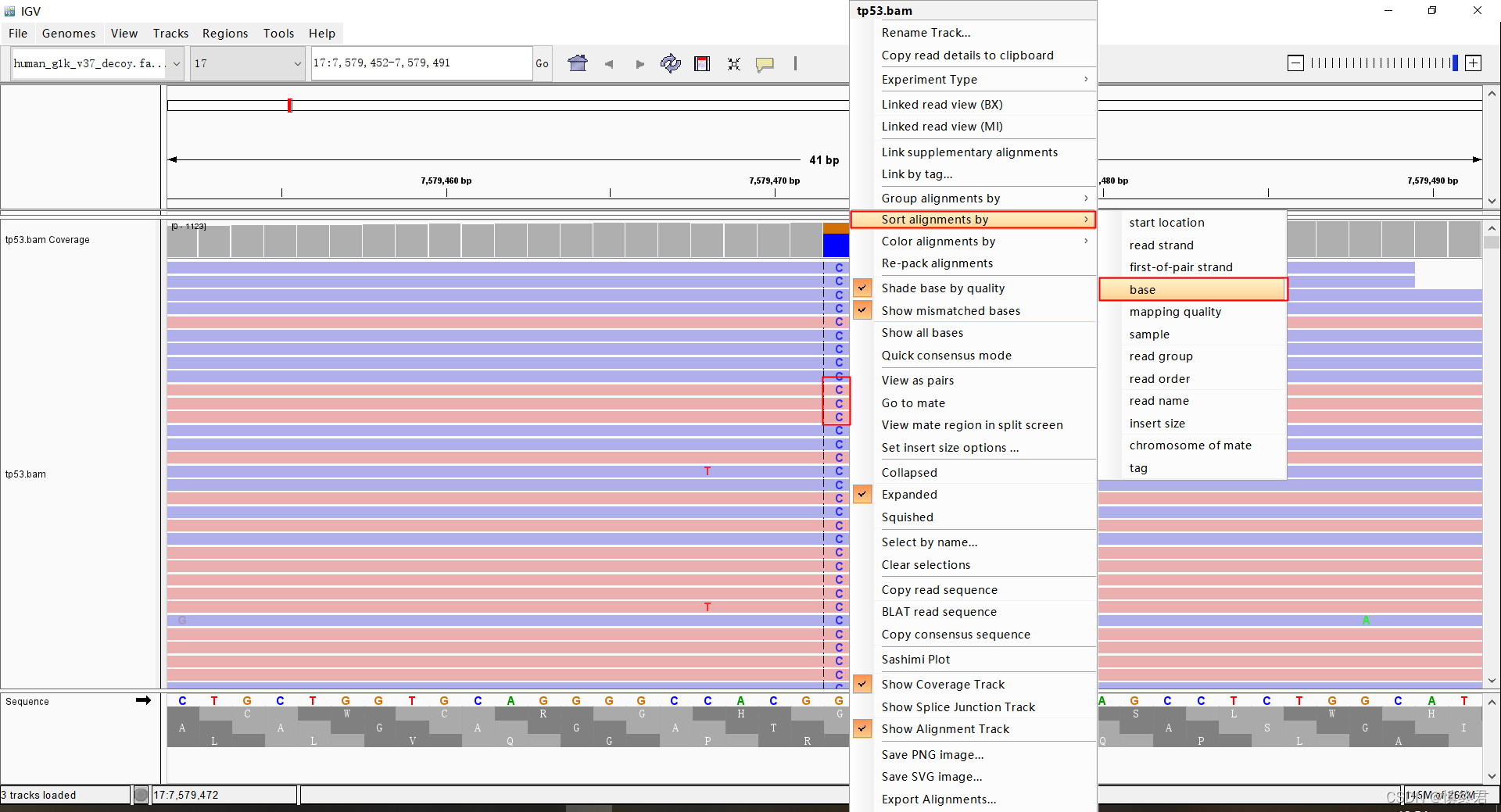
- 在中心线位置的碱基处右键选择按碱基排序,会优先显示变异碱基
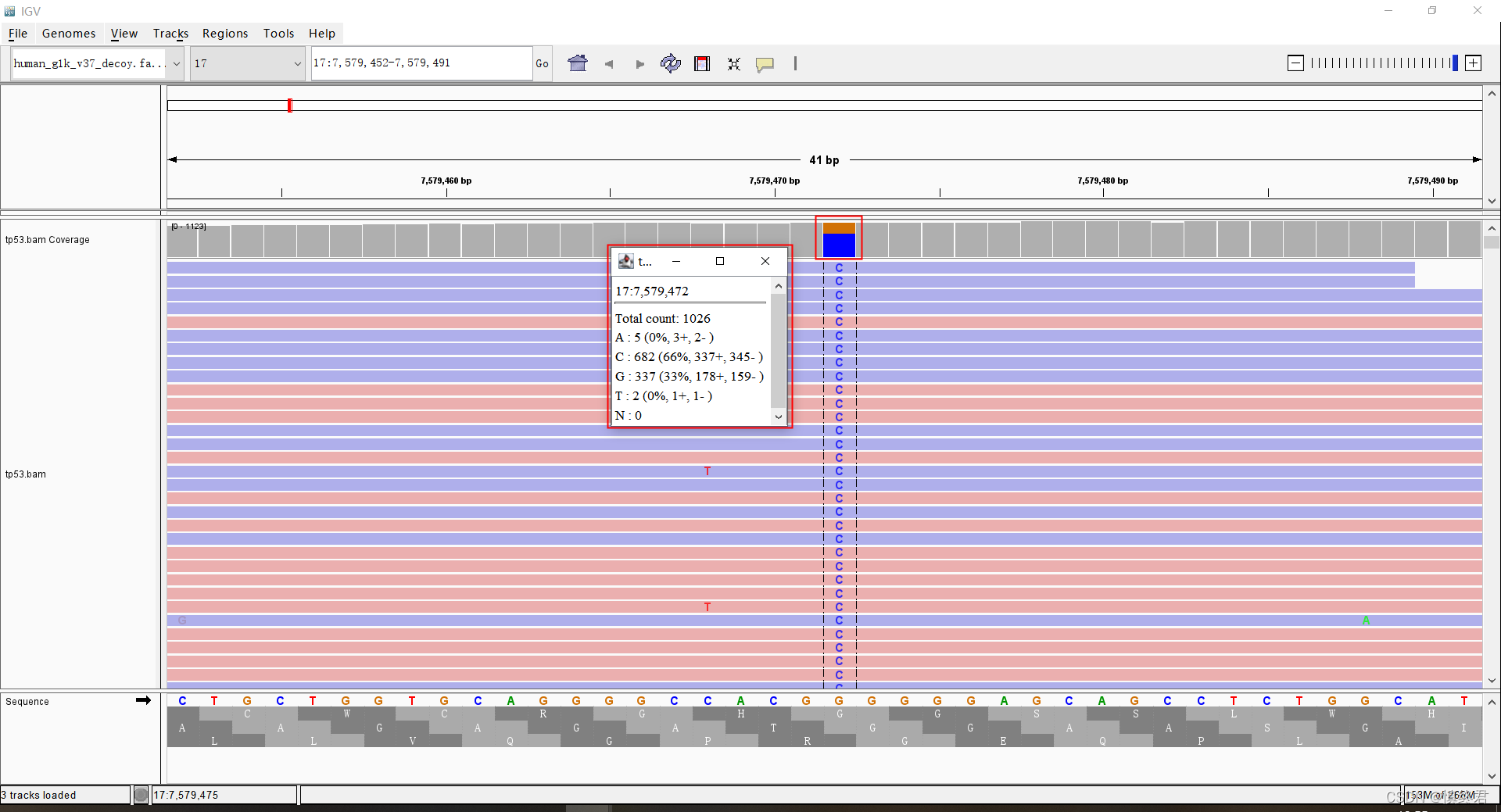
- 点击某一位置的覆盖度track,显示该位置各碱基变异分布情况
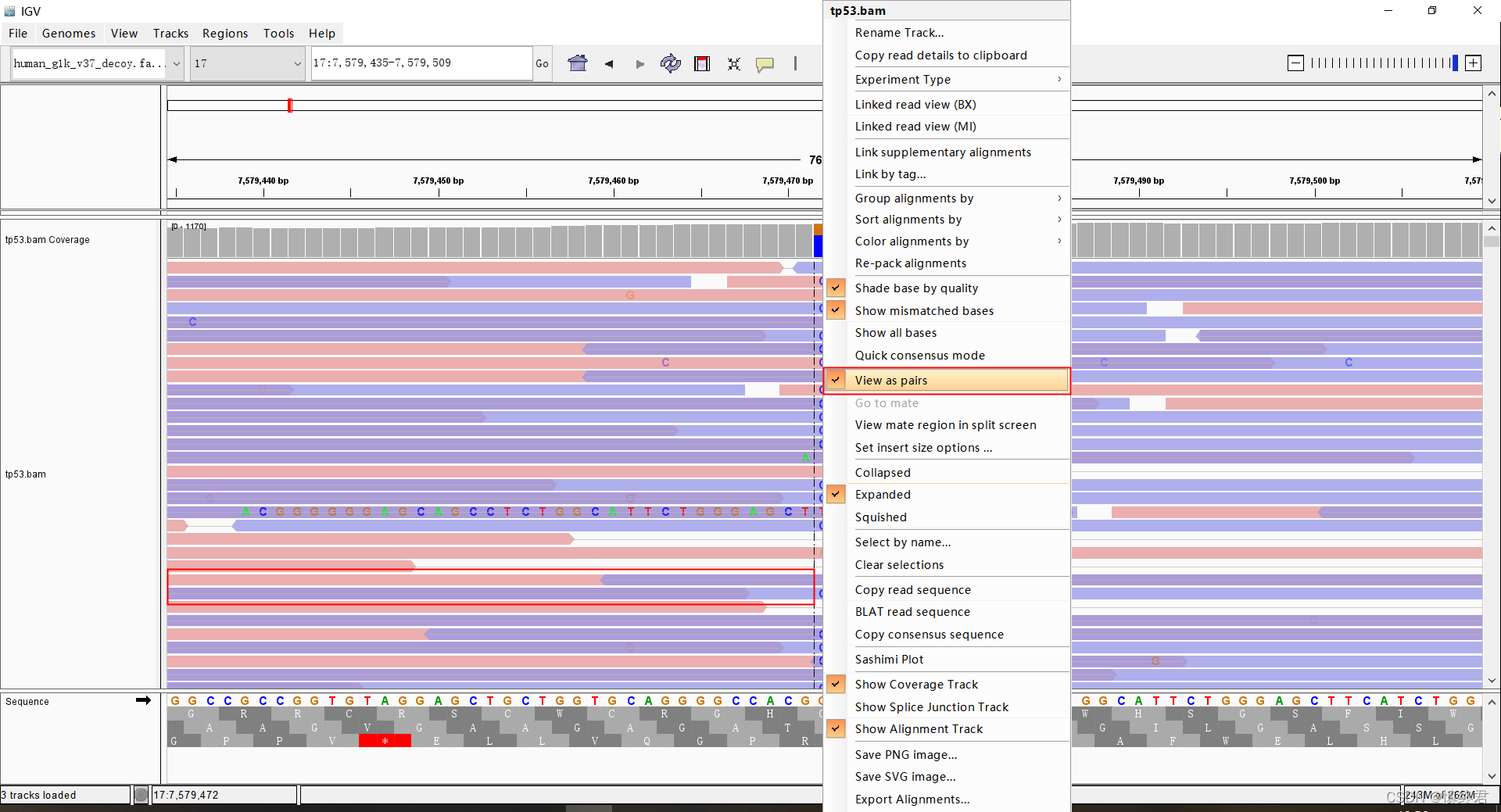
- 右键选择按成对reads查看,可以看到变异在双端测序的成对reads上的覆盖情况
























 2803
2803

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








