DecontX 是一种用于单细胞 RNA 测序数据的去除环境污染物(decontamination)的工具,主要用于减少由细胞外RNA造成的污染效应。

开发者在20年的文章中已经把这个工具适用的情况说的非常清楚了:简单来说就是基于微流控的单细胞技术会导致环境中污染的RNA增多,这种环境中的RNA是来自于自受压或经历细胞凋亡的细胞。当环境 RNA 掺入液滴中并与细胞的天然 mRNA一起被标记和扩增时,就会发生交叉污染。

DecontX可以通过贝叶斯统计模型对每个细胞的 RNA 读数进行推断,将原始数据分解为细胞内真实表达的 RNA 和污染的 RNA。该模型假设污染 RNA 来自于细胞群体的背景分布。进而估计每个细胞中污染 RNA 的比例,并根据污染的概率对原始表达矩阵进行校正,以生成一个含有去污染的表达矩阵(简单来说是给每个细胞一个污染评分,而使用者可以根据自己的需求调整筛选分值,分值是选择是在0-1之间)。
步骤流程
1.导入
rm(list = ls())
library(Seurat)
library(decontX)
library(dplyr)
load("sce.Rdata")
table(Idents(sce))
# CD14+ Mono CD8 T Naive CD4 T plasma B endothelial
# 638 476 1169 129 158
# FCGR3A+ Mono Fibroblasts NK DC
# 126 90 88 26
table(sce$seurat_clusters)
# 0 1 2 3 4 5 6 7 8 9 10 11
# 638 476 427 388 354 129 127 126 90 88 31 26
# check
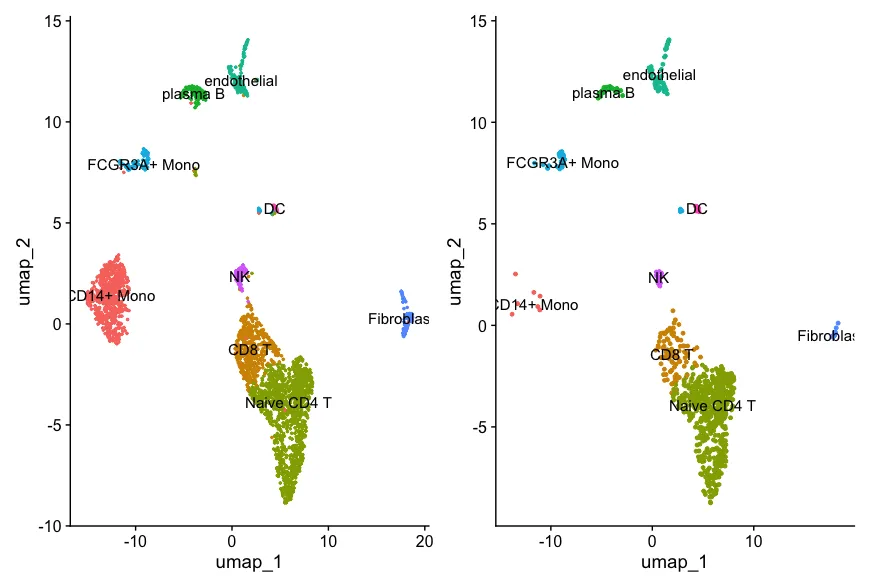
p1 <- DimPlot(sce,label = T)+NoLegend()
2.数据预处理
# 得到表达矩阵
set.seed(123)
counts <- GetAssayData(object = sce, slot = "counts")
decontX_res <- decontX(counts)
sce$contamination <- decontX_res$contamination
sce$contamination
# AGCCAATGTTTAAGGA-1 AGCCAATTCAGTGTGT-1 AGCCAATTCGTAGGGA-1
# 7.290200e-03 1.077294e-01 1.545725e-02
# AGCCACGAGAAGTATC-1 AGCCACGCAGTATGAA-1 AGCCACGGTGACTAAA-1
# 5.359679e-03 5.380567e-02 1.104379e-02
# AGCCACGTCCGTGTCT-1 AGCCAGCAGGATTCAA-1 AGCGATTCATGGCTGC-1
# 5.277364e-03 1.970192e-02 2.541087e-02
# AGCGATTGTAACCCGC-1 AGCGATTTCACCATGA-1 AGCGCCACACTTCAGA-1
# 3.808178e-02 2.057815e-02 4.581427e-02
# AGCGCTGCACCTAAAC-1 AGCGCTGGTTATGGTC-1 AGCGTATAGCAATTCC-1
# 1.266685e-02 7.821186e-02 5.331460e-05
# AGCGTATGTCGTGATT-1 AGCGTCGAGCCTCACG-1 AGCGTCGCACGCTTAA-1
# 1.563875e-02 2.488393e-03 6.933525e-02
# AGCTACACAACGACAG-1 AGCTACAGTCAGTTTG-1 AGCTACAGTCGGTGTC-1
# 9.982144e-01 2.014275e-02 1.181942e-02
# contamination值在0-1之间
sce_filt <- sce[,sce$contamination<0.01]
p2 <- DimPlot(sce_filt,label = T)+NoLegend()
p1+p2
contamination值设定范围是0-1, 这个值的设定就是自定的啦~ 其实也很主观hhh...
如果自己的数据有很多"毛刺样散在"细胞,就可以考虑使用这个工具进行过滤哦~
参考资料:
1、Decontamination of ambient RNA in single-cell RNA-seq with DecontX. Genome Biol. 2020 Mar 5;21(1):57. doi: 10.1186/s13059-020-1950-6 IF: 10.1 Q1 B1
2、decontX :
https://bioconductor.org/packages/release//bioc/manuals/decontX/man/decontX.pdf
https://github.com/campbio/decontX
3、生信技能树:https://mp.weixin.qq.com/s/ndt9Fsgg5dNxIOh9m7j9Bw
4、生信菜鸟团:https://mp.weixin.qq.com/s/UiO7AQczrcMdKENCWkLRCQ
致谢:感谢曾老师以及生信技能树团队全体成员。
注:若对内容有疑惑或者有发现明确错误的朋友,请联系后台(欢迎交流)。更多内容可关注公众号:生信方舟
- END -
























 5309
5309

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








