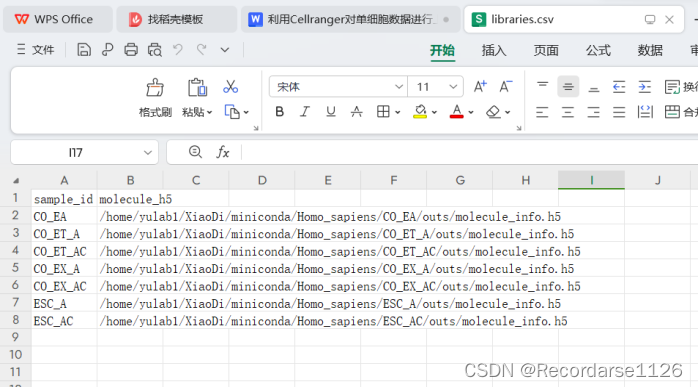
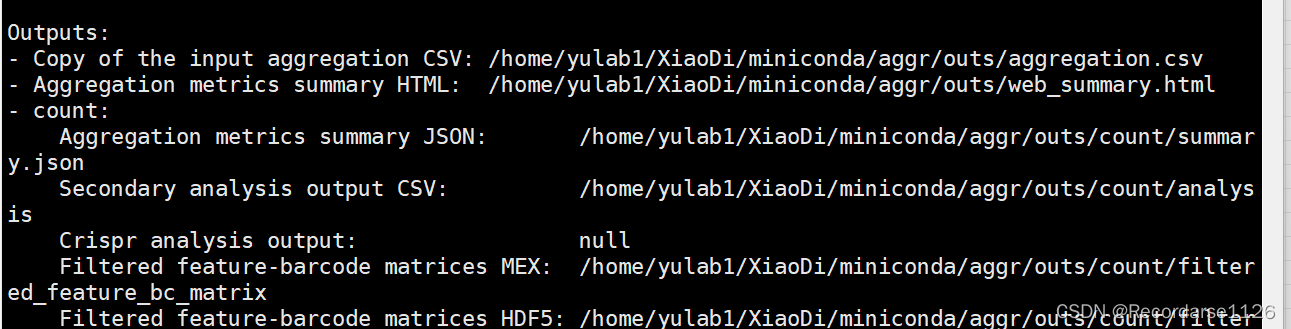
cellranger aggr --id=aggr \--csv=/home/yulab1/XiaoDi/miniconda/libraries.csv \--normalize=mapped错误显示:[error] Pipestance failed. Error log at:
aggr/SC_RNA_AGGREGATOR_CS/PARSE_AGGR_CSV/fork0/chnk0-u62e24c59ca/_errors
Log message:
The column at position 3 of the CSV file "/home/yulab1/XiaoDi/miniconda/libraries.csv" is empty, which is not allowed.
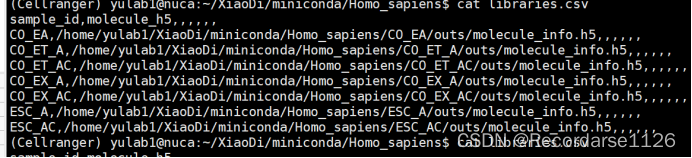
解决方案:多了一个空白列,可以cat一下,发现有空白列,删除空白列运行以上代码即可成功
 参考链接:
参考链接:























 1227
1227

 被折叠的 条评论
为什么被折叠?
被折叠的 条评论
为什么被折叠?








